Objectif:
Nous avons convenu avec l’équipe “PTM des protéines et réparation de l’ADN” de trouver une molécule disponible dans le commerce qui soit capable de bloquer l’interaction peptide-protéineSUMO1 / PIAS-SIM2. Pour cela, le PDB 6V7P a été utilisé, le site étant l’endroit où se fixe le peptide.
Résultats obtenus
10530 molécules ont été générées avec une affinité potentiellement intéressante soit un score_SMINA “minimizedAffinity” < -6.5 et une “efficiency” < -0.25 (efficiency = minimizedAffinity / nombre d’atomes lourds)
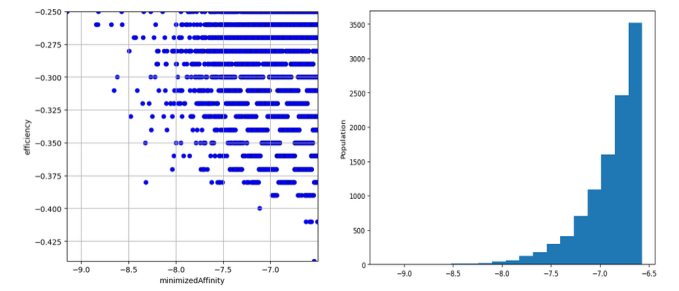
Les graphiques ci-contre indiquent la répartition des molécules obtenues.
Comparaison avec la Chembl
En comparant avec la Chembl, nous avons plus de chance de tomber sur une molécule disponible dans le commerce. Ainsi 47 molécules similaires ont pu être obtenus avec une similarité supérieure à 0.8.
Conclusion
Après redocking de ces molécules, une molécule très pertinente avec une efficiency et un logP de 3.3 a pu être proposée.

