La référence Chembl de la protéine est CHEMBL5567. Le site site a été défini à l’aide du PDB 5DWV.
Le site sera présenté de la façon suivante:
Etude de la molécule la plus active

smiles:Clc1ccc(C2=NO[C@H](Cc3ccccc3)C2)cc1
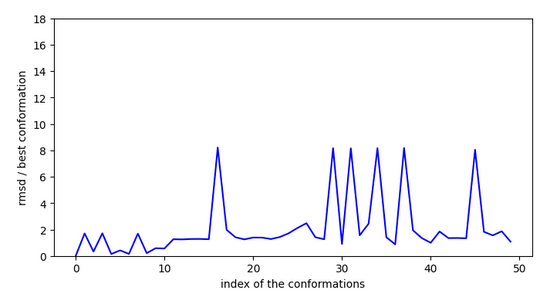
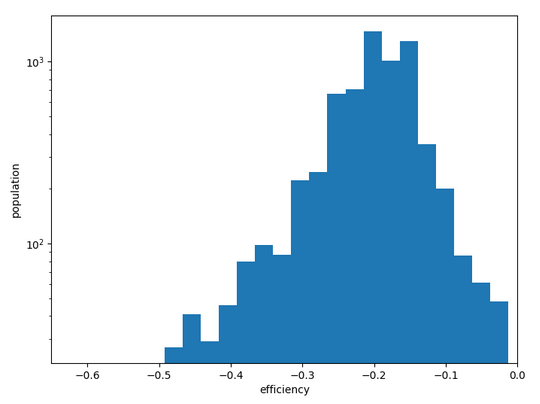
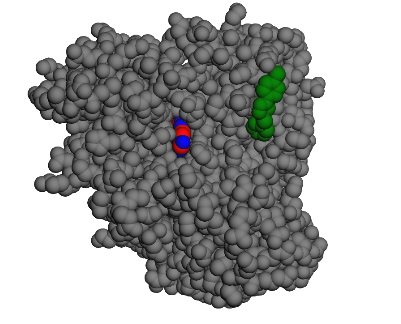
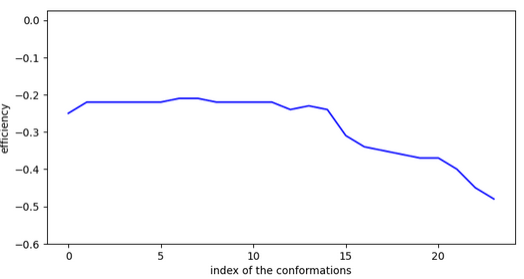
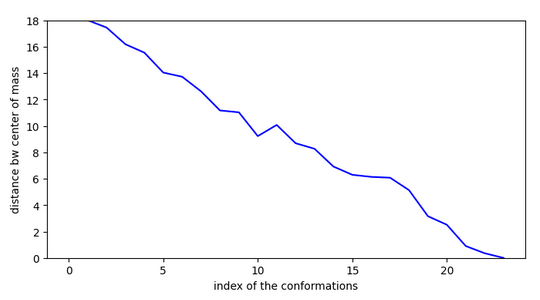
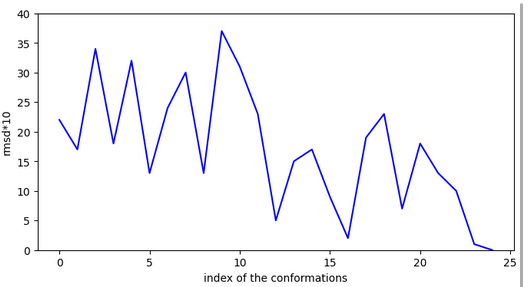
Conclusion: cette molécule est très active comme inhibiteur car elle possède des conformations stables proches les unes des autres et l’entrée dans le site ne présente pas d’activation.
Molécule qui ne fonctionne pas
–
Cc1cccc(C#Cc2ccccc2)n1

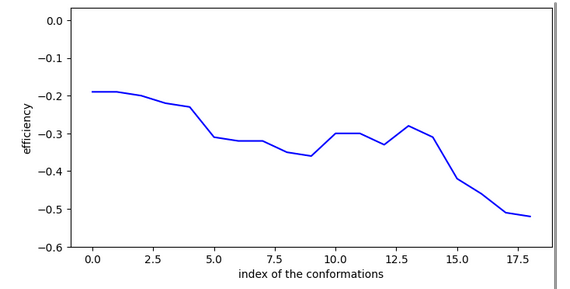
Cette molécule semble ne pas être active à cause d’un problème d’activation pour entrer dans le site.
–
COc1cccc(-c2cc(=O)c3ccccc3o2)c1N
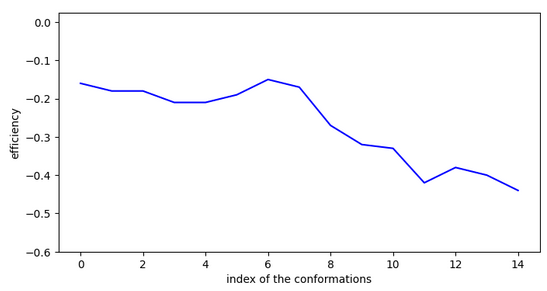
A priori, l’inactivité est liée à une activation, mais celle-ci ne semble pas systématique.
–

c1ccc(C[C@@H]2CC(c3cccc4ccccc34)=NO2)cc1
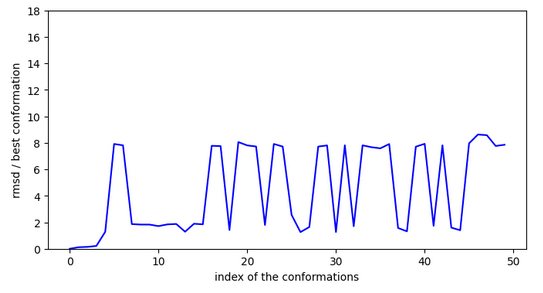
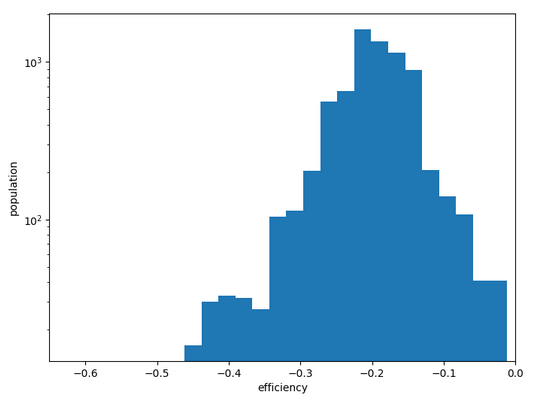
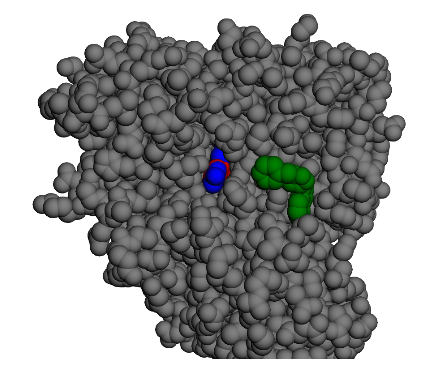
Conformation ci-dessus liée aux graphiques ci-contre. CI-dessous, autre conformation de départ mais demande des sauts plus importans.
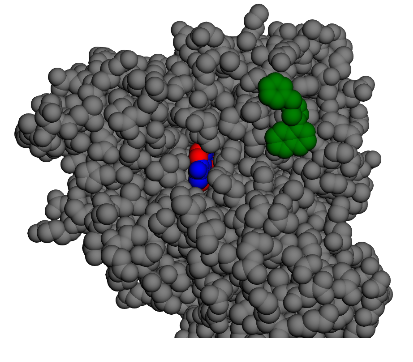
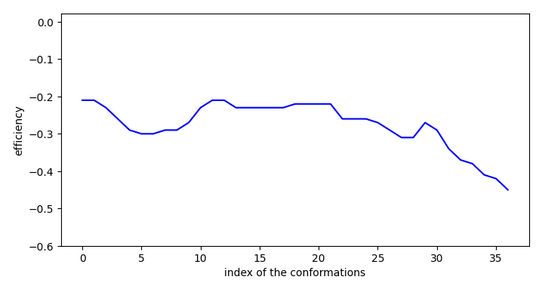
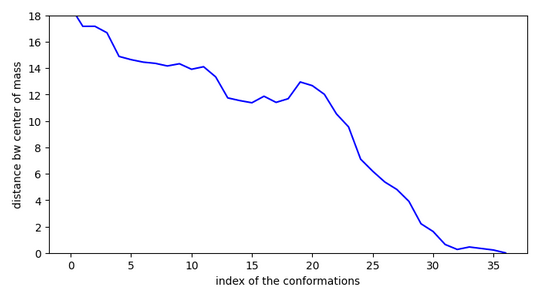
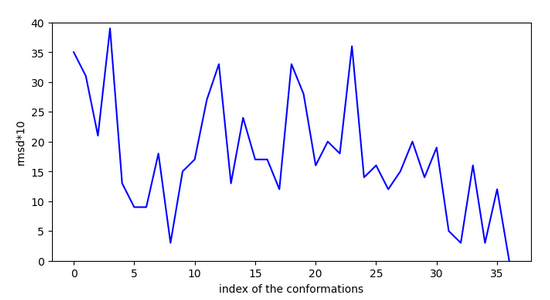
Cette molécule ne serait pas très active car elle doit franchir une activation à l’entrée du site.
Résultat de la génération de molécules
Sur les 62338 valeurs expérimentales sur la Luciferin présentes dans la Chembl:
– 2 030 molécules uniques sont inactives
– 25 510 sont actives
127 sont données à la fois active et inactives
: CHEMBL1269779, CHEMBL1299412, CHEMBL1301753, CHEMBL1301776, CHEMBL1303292, CHEMBL1303835, CHEMBL1305810, CHEMBL1307028, CHEMBL1309478, CHEMBL1311937, CHEMBL1313232, CHEMBL1327749, CHEMBL1328395, CHEMBL1330076, CHEMBL1332688, CHEMBL1338057, CHEMBL1338658, CHEMBL1342109, CHEMBL1346564, CHEMBL1349226, CHEMBL1352348, CHEMBL1353358, CHEMBL1360154, CHEMBL1368187, CHEMBL1369231, CHEMBL1369270, CHEMBL1369691, CHEMBL1370087, CHEMBL1374135, CHEMBL1375202, CHEMBL1380161, CHEMBL1384906, CHEMBL1387309, CHEMBL1389449, CHEMBL1390799, CHEMBL1390836, CHEMBL1402831, CHEMBL1409173, CHEMBL1409752, CHEMBL1410454, CHEMBL1416658, CHEMBL1427279, CHEMBL1427687, CHEMBL1427979, CHEMBL1429929, CHEMBL1432374, CHEMBL1450780, CHEMBL1452026, CHEMBL1452108, CHEMBL1452243, CHEMBL1453291, CHEMBL1453801, CHEMBL1454850, CHEMBL1456942, CHEMBL1457010, CHEMBL1457060, CHEMBL1458659, CHEMBL1459767, CHEMBL1463600, CHEMBL1464039, CHEMBL1466311, CHEMBL1479862, CHEMBL1482541, CHEMBL1490104, CHEMBL1498744, CHEMBL1502354, CHEMBL1502358, CHEMBL1502435, CHEMBL1504592, CHEMBL1506379, CHEMBL1511385, CHEMBL1518672, CHEMBL1518774, CHEMBL1521476, CHEMBL1528232, CHEMBL1533919, CHEMBL1535200, CHEMBL1545657, CHEMBL1547757, CHEMBL1550917, CHEMBL1556732, CHEMBL1558433, CHEMBL1558550, CHEMBL1560675, CHEMBL1560698, CHEMBL1560969, CHEMBL1567220, CHEMBL1568027, CHEMBL1572538, CHEMBL1576870, CHEMBL1577306, CHEMBL1578584, CHEMBL1581468, CHEMBL1582610, CHEMBL1585105, CHEMBL1585869, CHEMBL1587583, CHEMBL1595336, CHEMBL1601294, CHEMBL1602841, CHEMBL1606813, CHEMBL1609758, CHEMBL1611128, CHEMBL1612413, CHEMBL1612693, CHEMBL191750, CHEMBL1971760, CHEMBL1973921, CHEMBL1988310, CHEMBL259421, CHEMBL261118, CHEMBL265715, CHEMBL285540, CHEMBL3191859, CHEMBL3193741, CHEMBL3196633, CHEMBL3197960, CHEMBL3207928, CHEMBL3209179, CHEMBL3209305, CHEMBL3210725, CHEMBL3212753, CHEMBL3212828, CHEMBL3213419, CHEMBL410484, CHEMBL411085, CHEMBL572346,
Emolgine a généré 1 335 852 molécules avec un score SMINA < – 6.5. Parmi celles-ci:
– 2251 molécules sont similaires à celles générées avec une similarité supérieure à 60% (tanimoto).
– 509 molécules sont similaires à celles générées avec une similarité supérieure à 90% (tanimoto).
Parmi les 509 , seules les 5 suivantes ont été notées inactives:
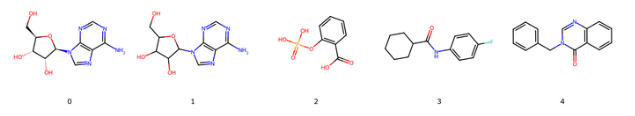
Les résultats expérimentaux associé au 504 molécules restantes sont au nombre de 660:
– 430 actifs et 214 “inconclusives”.
– 312 molécules sont annotées une fois actives
– 195 molécules sont annotées sytématiquement “inconclusives”.

